近日,我校前沿交叉学科研究院生物学研究中心夏庆友教授团队在国际学术期刊《CRISPR》上在线发表了最新科研成果“Deep sequencing reveals the comprehensive CRISPR/Cas9 editing spectrum in Bombyx mori”。
CRISPR/Cas9系统依靠其强大的DNA特异编辑功能及其在疾病治疗方面的潜在能力,迅速在生物领域广泛应用并产生革命性变革。传统上,人们认为该系统在靶位点引入了随机的缺失或插入(indels)。我们在对家蚕16个个体中9个不同的sgRNA的共计31161个靶位点编辑事件进行综合分析之后,发现Cas9系统在引入突变的事件上并不是传统认为的完全随机的indels,而是存在一定的规律性。CRISPR/Cas9系统的编辑效率在不同的sgRNA序列、不同个体、不同方向中存在差异。编辑事件以小片段缺失为主,其次是小片段的替换或插入。最大概率的突变事件是:在两个微同源序列存在的情况下的片段缺失及微同源序列不存在时在切割位点的单碱基缺失。插入突变的形成机制包括:从自由基因组碎片中的直接获得、断裂末端的复制、相邻片段的重复、或自由核苷酸碱基的随机添加。以上结果表明:CRISPR/Cas9系统在靶位点的编辑图谱是可复预测的。我们的研究结果加深了对Cas9介导的编辑事件的理解,便于更好的设计基因编辑实验,以及阐述了家蚕中DNA双链断裂后的修复过程。
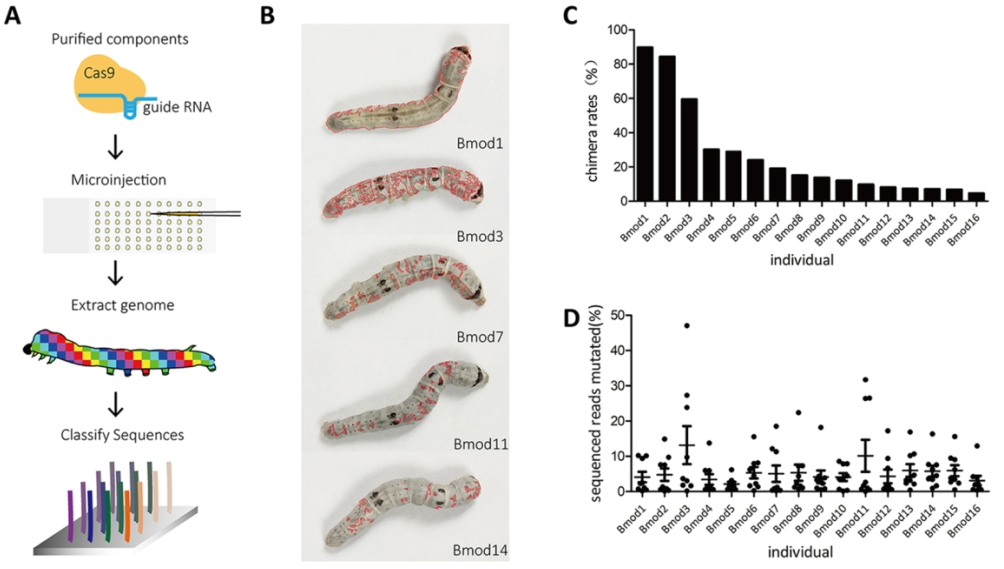
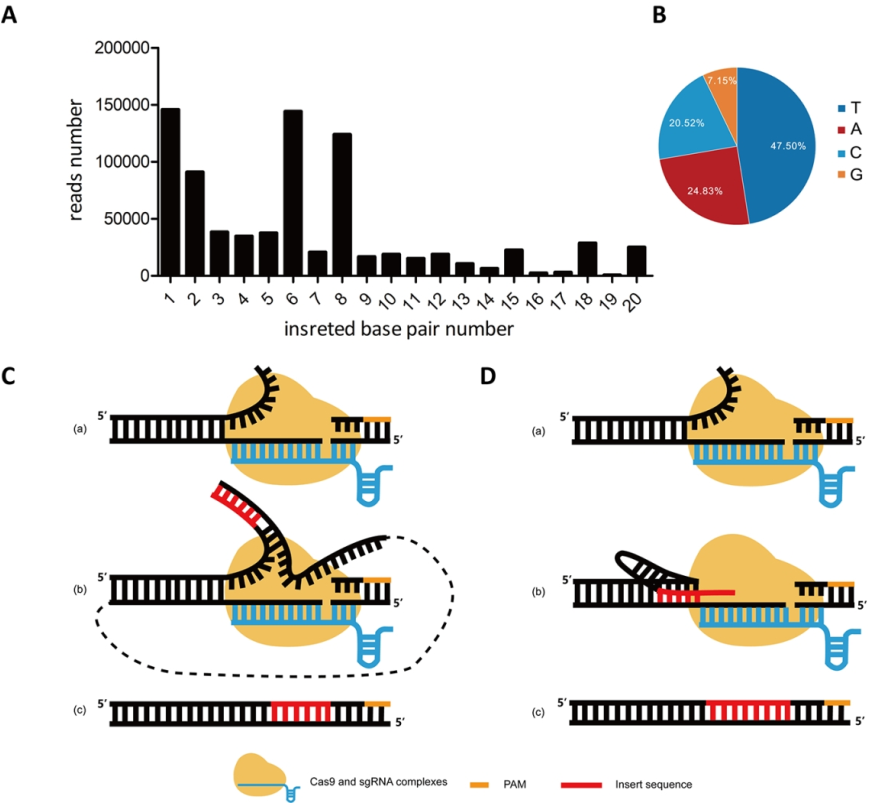
西南大学马三垣副教授和硕士生王奥铭为论文的共同一作,夏庆友教授和马三垣副教授为通讯作者,西南大学为第一完成单位。该研究受到国家自然科学基金项目和重庆市自然科学基金项目的资助。
文章链接:https://www.liebertpub.com/doi/10.1089/crispr.2021.0003